En mode Hercule Poirot.
Souris par-ci, souris par-là.
La variante Omicron du coronavirus pourrait-elle avoir évolué chez la souris ? De nouvelles recherches indiquent que la variante hautement infectieuse du SRAS-CoV-2 connue sous le nom d’Omicron pourrait être passée de l’homme à l’animal, et inversement.
Une étude évaluée par des pairs et intitulée «
Evidence for a mouse origin of the SARS-CoV-2 Omicron variant », publiée dans le numéro du mois dernier du
Journal of Genetics and Genomics, a examiné l’accumulation rapide de mutations dans la variante Omicron et a tenté de comprendre comment et pourquoi le virus a acquis les mutations qu’il a acquises en si peu de temps.
La mutation Omicron a été détectée pour la première fois par des scientifiques sud-africains le 24 novembre 2021 et a été classée comme une variante d’intérêt par l’Organisation mondiale de la santé, principalement en raison de sa propagation rapide et d’un nombre élevé de mutations inhabituelles.
Alors que deux théories dominantes existaient déjà parmi les scientifiques pour expliquer comment Omicron s’est développé exactement, une équipe de chercheurs de l’Académie chinoise des sciences à Pékin a trouvé des preuves d’une troisième théorie qui suggère qu’Omicron a pu muter et évoluer chez les souris.
La première théorie concernant la façon dont Omicron a évolué de façon si importante sans être détecté jusqu’en novembre émet l’hypothèse qu’il aurait pu se propager de façon cryptique, se développant et mutant dans une population où la surveillance virale et la technologie de séquençage étaient insuffisantes. Dans ce cas, il aurait pu se propager sans être détecté jusqu’à ce qu’il atteigne l’Afrique du Sud, où des technologies avancées l’ont repéré. Toutefois, les chercheurs ont suggéré que ce scénario est hautement improbable, car les étapes intermédiaires de l’évolution d’Omicron auraient quand même dû être captées par des personnes voyageant d’un pays à l’autre.
La deuxième hypothèse suggère qu’Omicron pourrait s’être développé chez une seule personne, un patient atteint d’une infection chronique qui a fourni un environnement hôte approprié pour que le virus puisse muter et s’adapter sur une longue période. Ce phénomène a déjà été observé chez des patients atteints d’une infection chronique par le COVID-19 et dont le système immunitaire est compromis, mais jamais dans une mesure aussi importante que celle observée chez Omicron, qui a accumulé plus de 50 mutations.
La troisième option. Insatisfaite de ces deux options, l’équipe de recherche de Pékin a entrepris d’étudier la possibilité d’une troisième option, selon laquelle une mutation antérieure serait passée de l’homme à la souris dans le courant de l’année 2020, aurait muté discrètement en se propageant parmi les souris pendant plus d’un an, avant de revenir à l’homme vers la fin de l’année 2021.
Depuis le début de la pandémie, le SRAS-CoV-2 a prouvé à plusieurs reprises qu’il était capable de se propager à d’autres espèces avec une relative facilité. Il a été détecté chez des chats et des chiens, des hyènes et des hippopotames, des furets et des hamsters, et même chez un léopard sauvage. En fait, des millions de visons ont été abattus dans des fermes en Europe en 2020 après que l’on ait découvert que le virus circulait parmi les espèces. Il n’est donc pas impossible de suggérer qu’il ait pu passer aux souris à un moment donné au cours des deux dernières années.
Afin de prouver leur hypothèse, l’équipe de recherche a identifié les mutations acquises par Omicron avant son apparition et a testé si le spectre moléculaire des mutations correspondait ou non à l’environnement cellulaire des hôtes humains.
Selon des études antérieures menées par la même équipe, les génomes de nombreux virus à ARN mutés ont tendance à acquérir davantage de mutations dans des bases particulières, en fonction de l’espèce dans laquelle ils se répliquent. Cela signifie que les génomes des virus dépendent de processus et de mécanismes spécifiques à l’espèce pour se diviser et évoluer. Par conséquent, des types de mutations spécifiques seront très répandus en fonction de l’espèce dans laquelle le virus a évolué.
Dans ce cas, en testant les mutations d’Omicron avant l’épidémie, l’équipe de recherche a constaté des dissemblances importantes entre le spectre moléculaire d’Omicron et le spectre moléculaire de plusieurs variantes différentes connues pour avoir évolué chez l’homme, y compris celui de trois variantes qui ont évolué chez des patients chroniques atteints de COVID-19.Par conséquent, la structure moléculaire d’Omicron était incompatible avec le spectre moléculaire standard des variants qui se sont développés chez l’homme.
À la lumière de ce constat, les scientifiques ont cherché à déterminer quelles espèces d’hôtes non humaines auraient pu être à l’origine des mutations du virus. Pour ce faire, ils ont récupéré 17 séquences de virus de l’hépatite murine (souris), 13 coronavirus canins, 54 coronavirus félins, 23 coronavirus bovins (bovins) et 110 coronavirus porcins (porcins) Delta.
L’équipe de recherche s’est ensuite attachée à comparer le spectre moléculaire d’Omicron à celui de ces séquences, en utilisant des analyses basées sur l’amarrage (docking) moléculaire afin de déterminer si les mutations de la protéine de pointe d’Omicron pouvaient être associées à des adaptations réalisées par le virus chez d’autres espèces hôtes. En effet, les chercheurs ont constaté que les mutations de la protéine de pointe Omicron présentaient un chevauchement important avec les mutations du virus SARS-CoV-2 adapté à la souris.
Plusieurs des mutations d’Omicron ont permis à la variante du coronavirus de se lier étroitement aux souris et aux rats, mais n’auraient pas été aussi efficaces lorsqu’il s’agissait de se lier aux humains, ce qui rend très improbable leur développement ailleurs que chez les rongeurs. Alors qu’à l’origine, au début de la pandémie, on avait signalé que les souris étaient de mauvais hôtes pour le virus, l’apparition de différents variants a permis à plusieurs d’entre eux d’infecter des souris.
Par exemple, les variants portant la mutation de pointe spécifique N501Y étaient relativement courants chez les patients humains, mais ils étaient également capables d’infecter les souris, ce qui permettait potentiellement à la maladie de passer de l’homme à la souris et de se propager parmi les espèces de rongeurs.
Une fois le passage de l’homme à la souris effectué, l’infection aurait pu se propager librement chez les souris, évoluant et s’adaptant de manière indépendante, alors même que d’autres variantes, comme Delta, continuaient à se propager chez l’homme, jusqu’à ce qu’une occasion se présente pour la variante de la souris, alors complètement mutée, de revenir dans l’espèce humaine.
En outre, la recherche a suggéré que, tout en évoluant chez les souris, le virus a développé des mutations associées à l’échappement immunitaire, ce qui explique sa propagation rapide chez l’homme.
Cette étude, souligne l’équipe de recherche, met en évidence « la nécessité de la surveillance et du séquençage des virus chez les animaux, en particulier ceux qui sont en contact étroit avec les humains. » En effet, les humains constituent le plus grand groupe connu de porteurs du SRAS-CoV-2 et entrent fréquemment en contact avec d’autres animaux, qu’il s’agisse d’animaux de compagnie, d’animaux sauvages ou de bétail.
« Étant donné la capacité du SRAS-CoV-2 à passer d’une espèce à l’autre, il est probable que les populations mondiales seront confrontées à d’autres variantes d’origine animale jusqu’à ce que la pandémie soit bien maîtrisée », conclut l’étude.
Voir la pièce jointe 121653
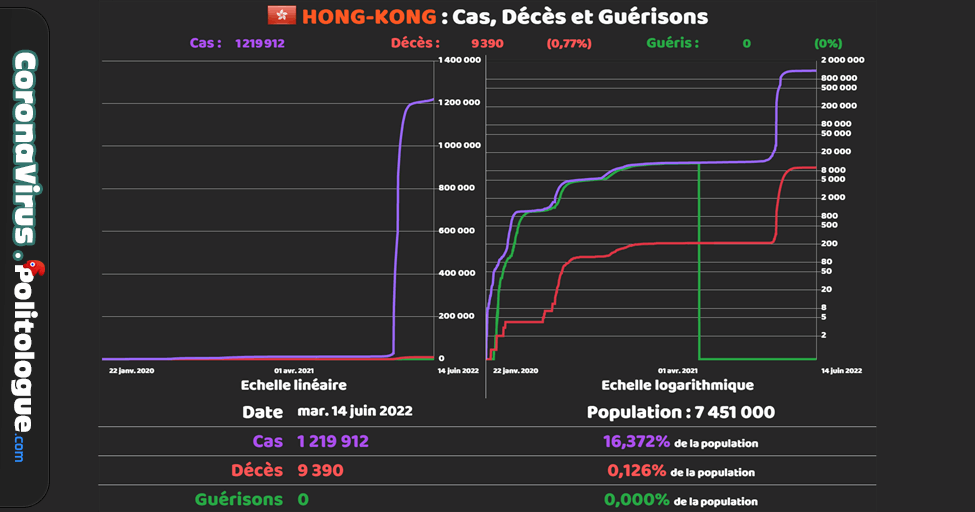
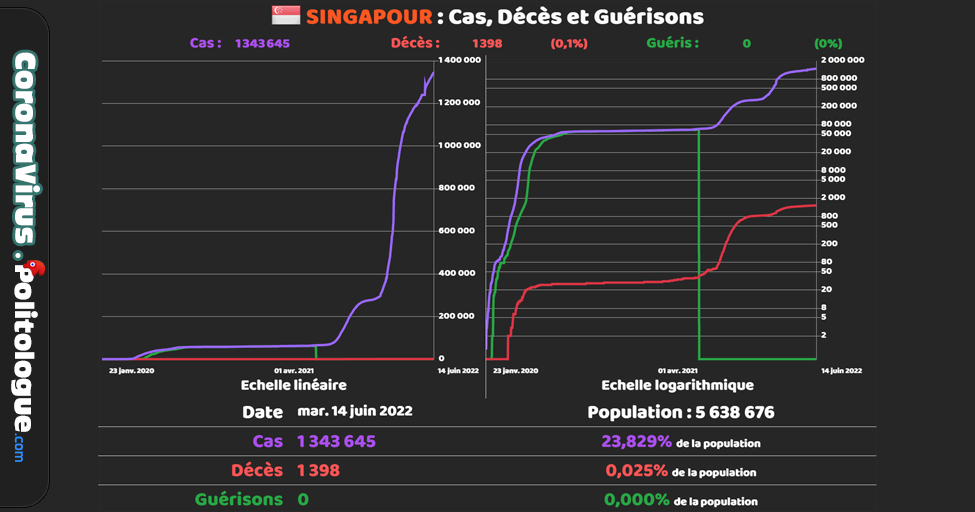
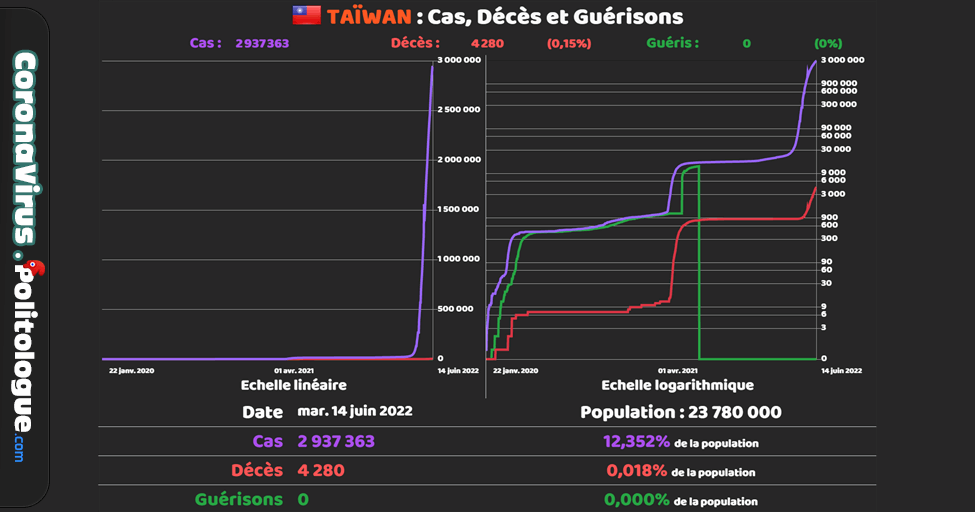





















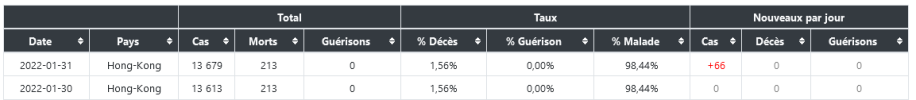

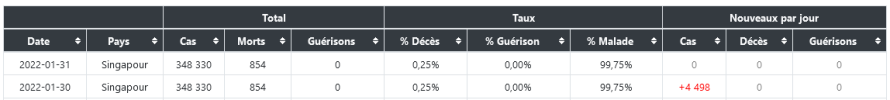

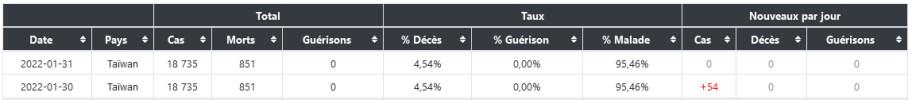




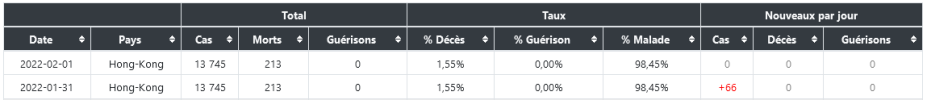






 Si les personnes contaminees jettent les masques usages dans les egouts par exemple les rats grand amateurs de matieres de ce genre surtout impregrees d'odeurs humaines , et vu que ces bestioles courrent de partout dans de nombreux endroits souillent aliments et autres a leurs contacts et dejections , il y a par exemple + de 6 millions de rats a Paris ...
Si les personnes contaminees jettent les masques usages dans les egouts par exemple les rats grand amateurs de matieres de ce genre surtout impregrees d'odeurs humaines , et vu que ces bestioles courrent de partout dans de nombreux endroits souillent aliments et autres a leurs contacts et dejections , il y a par exemple + de 6 millions de rats a Paris ...